विगत १० वर्षमा, CRISPR मा आधारित जीन सम्पादन प्रविधि द्रुत रूपमा विकसित भएको छ, र मानव क्लिनिकल परीक्षणहरूमा आनुवंशिक रोग र क्यान्सरको उपचारमा सफलतापूर्वक लागू गरिएको छ।उही समयमा, विश्वभरका वैज्ञानिकहरू विद्यमान जीन सम्पादन उपकरणहरू र निर्णायकहरूको समस्याहरू समाधान गर्न जीन सम्पादन क्षमताका साथ नयाँ नयाँ उपकरणहरू निरन्तर ट्याप गरिरहेका छन्।
सेप्टेम्बर 2021 मा, Zhang Feng को टोलीले विज्ञान जर्नल [1] मा एउटा पेपर प्रकाशित गर्यो र पत्ता लगायो कि ट्रान्सपोस्टरहरूको विस्तृत श्रृंखलाले RNA निर्देशित न्यूक्लिक एसिड इन्जाइमहरू कोड गरेको छ र यसलाई ओमेगा प्रणाली (ISCB, ISRB, TNP8 सहित) नाम दिएको छ।अध्ययनले यो पनि पत्ता लगायो कि ओमेगा प्रणालीले काट्ने DNA दोहोरो चेन, अर्थात् ωRNA लाई मार्गदर्शन गर्न RNA को एक खण्ड प्रयोग गर्दछ।अझ महत्त्वपूर्ण कुरा, यी न्यूक्लिक एसिड इन्जाइमहरू धेरै सानो छन्, CAS9 को मात्र 30%, जसको मतलब तिनीहरू कोशिकाहरूमा डेलिभर हुने सम्भावना बढी हुन सक्छ।

अक्टोबर 12, 2022 मा, Zhang Feng को टोली नेचर जर्नल मा प्रकाशित: ωrna र लक्ष्य DNA संग कम्प्लेक्स मा ओमेगा Nickase ISRB को संरचना [2]।
अध्ययनले ISRB-ωRNA को जमेको इलेक्ट्रोन माइक्रोस्कोप संरचना र ओमेगा प्रणालीमा लक्षित DNA जटिलतालाई थप विश्लेषण गर्यो।
ISCB CAS9 को पूर्वज हो, र ISRB ISCB को HNH न्यूक्लिक एसिड डोमेनको कमीको समान वस्तु हो, त्यसैले आकार सानो छ, लगभग 350 एमिनो एसिडहरू।DNA ले थप विकास र ईन्जिनियरिङ् रूपान्तरणको लागि आधार पनि प्रदान गर्दछ।

RNA-निर्देशित IsrB ओमेगा परिवारको सदस्य हो जुन IS200/IS605 superfamily of transposons द्वारा इन्कोड गरिएको छ।फाइलोजेनेटिक विश्लेषण र साझा अद्वितीय डोमेनहरूबाट, IsrB IscB को अग्रसर हुन सक्छ, जुन Cas9 को पूर्वज हो।
मे २०२२ मा, कर्नेल युनिभर्सिटीको लभली ड्र्यागन प्रयोगशालाले जर्नल साइन्स [३] मा IscB-ωRNA को संरचना र यसको DNA काट्ने मेकानिजमको विश्लेषण गरी एउटा पेपर प्रकाशित गर्यो।

IscB र Cas9 सँग तुलना गर्दा, IsrB सँग HNH nuclease डोमेन, REC लोब, र PAM अनुक्रम-अन्तरक्रिया गर्ने डोमेनहरूको धेरै कमी छ, त्यसैले IsrB Cas9 भन्दा धेरै सानो छ (केवल 350 एमिनो एसिडहरू)।यद्यपि, IsrB को सानो आकार एक अपेक्षाकृत ठूलो गाइड RNA द्वारा सन्तुलित छ (यसको ओमेगा RNA लगभग 300 nt लामो छ)।
Zhang Feng को टोलीले नम-तातो एनारोबिक ब्याक्टेरियम Desulfovirgula thermocuniculi र यसको ωRNA र लक्षित DNA को जटिलबाट IsrB (DtIsrB) को क्रायो-इलेक्ट्रोन माइक्रोस्कोप संरचनाको विश्लेषण गर्यो।संरचनात्मक विश्लेषणले देखायो कि IsrB प्रोटिनको समग्र संरचनाले Cas9 प्रोटीनसँग ब्याकबोन संरचना साझा गरेको छ।
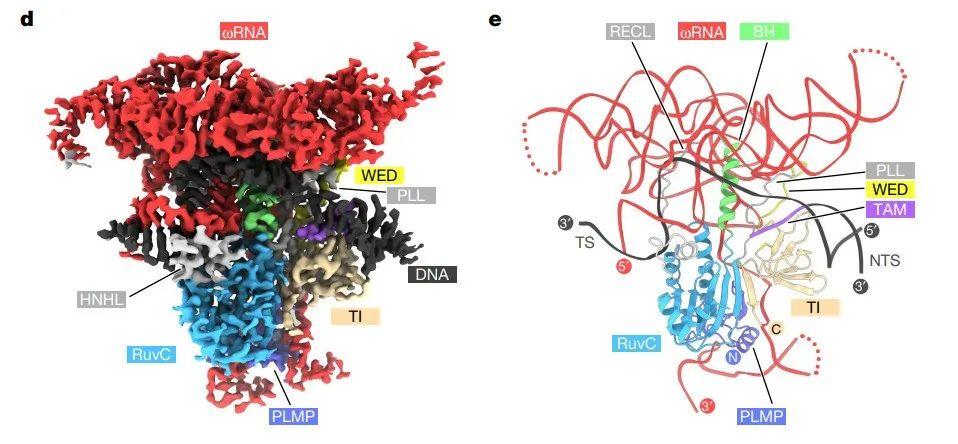
तर भिन्नता यो हो कि Cas9 ले लक्ष्य पहिचानको सुविधाको लागि REC लोब प्रयोग गर्दछ, जबकि IsrB यसको ωRNA मा निर्भर गर्दछ, जसको एक भाग REC जस्तै कार्य गर्ने जटिल त्रि-आयामी संरचना बनाउँछ।
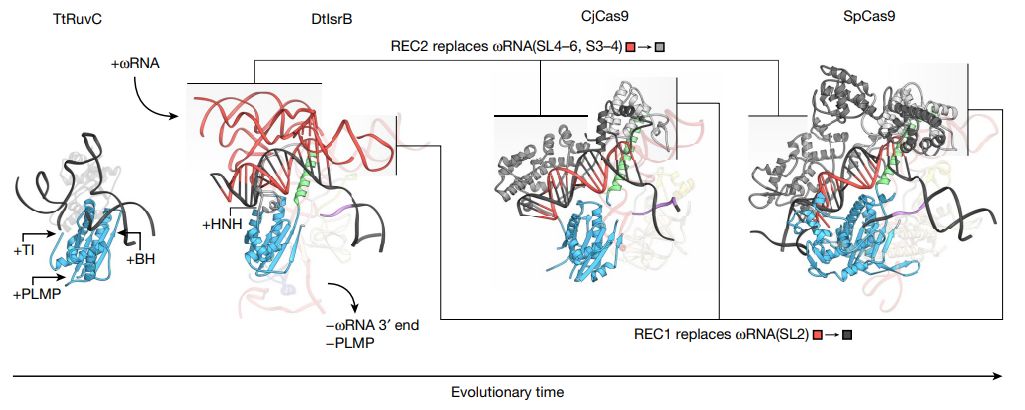
RuvC बाट विकासको क्रममा IsrB र Cas9 को संरचनात्मक परिवर्तनहरू अझ राम्ररी बुझ्नको लागि, Zhang Feng को टोलीले RuvC (TtRuvC), IsrB, CjCas9 र SpCas9 को थर्मस थर्मोफिलसको लक्षित DNA-बाध्यकारी संरचनाहरूको तुलना गर्यो।
IsrB र यसको ωRNA को संरचनात्मक विश्लेषणले IsrB-ωRNA ले संयुक्त रूपमा लक्षित DNA लाई कसरी चिन्ने र क्लीभ गर्छ भन्ने कुरा स्पष्ट गर्दछ, र यो सानो न्यूक्लिजको थप विकास र इन्जिनियरिङको लागि आधार पनि प्रदान गर्दछ।अन्य आरएनए-निर्देशित प्रणालीहरूसँगको तुलनाहरूले प्रोटीन र आरएनएहरू बीचको कार्यात्मक अन्तरक्रियालाई हाइलाइट गर्दछ, जीवविज्ञान र यी विविध प्रणालीहरूको विकासको हाम्रो बुझाइलाई अगाडि बढाउँछ।
लिङ्कहरू:
1.https://www.science.org/doi/10.1126/science.abj6856
2.https://www.science.org/doi/10.1126/science.abq7220
3.https://www.nature.com/articles/s41586-022-05324-6
पोस्ट समय: अक्टोबर-14-2022








